ウニ胚や幼生の神経細胞は、細胞数が少なく、神経分化の流れや分子制御を詳細に追跡することが容易ではありません。今回、バフンウニについて、発生段階ごとの単一細胞RNA-seqアトラス(細胞分布データ集)を構築し、誰もが手軽に1細胞レベルでの遺伝子発現を調べられる形で公開しました。
単一細胞RNAシーケンス(single-cell RNA-seq; scRNA-seq)は、個々の細胞がどの遺伝子を発現しているかを網羅的に解析できる強力な手法です。生物の発生過程では、同じ胚の中でも細胞が多様な運命へ分岐していきますが、scRNA-seqを用いると、細胞集団全体を平均した解析(バルクRNA-seq)だけでは捉えきれない「細胞ごとの違い」を明らかにすることができます。しかしながら、ウニ胚や幼生の神経細胞のように細胞数が少ない細胞集団は、解析データの中で埋もれやすく、神経分化の流れや分子制御を詳細に追跡することは困難です。
本研究では、バフンウニHemicentrotus pulcherrimusの胚発生(受精後24〜96時間)にわたるscRNA-seqアトラス(細胞分布データ集)を構築し、発生段階に沿った細胞状態の変化を単一細胞レベルで体系的に整理しました。さらに、隣接する細胞の相互作用を薬理学的に阻害して、神経分化を増強させることで、通常条件では検出が難しい神経系の細胞集団や関連遺伝子群をより明瞭に捉えることに成功しました。得られたデータは、日本産ウニのゲノムデータベース(HpBase)にて公開し、計算解析に不慣れな研究者でも直感的に遺伝子発現を探索できる研究基盤として整備しました。
研究代表者
筑波大学生命環境系
谷口 俊介 准教授
千葉大学大学院医学研究院
露崎 弘毅 特任講師
広島大学ゲノム編集イノベーションセンター
山本 卓 教授
国立遺伝学研究所遺伝情報分析研究室
池尾 一穂 准教授
研究の背景
ウニは古くから発生生物学注1)の代表的な実験材料として用いられ、受精・卵割・原腸形成・細胞運命決定といった基本原理の解明に大きく貢献してきました。透明で操作しやすい胚を大量に得られる点に加え、外部からの処理や観察を組み合わせた実験設計に適しているという特徴があります。しかしながら、マウスやショウジョウバエなどの典型的なモデル生物と比較すると、系統維持や遺伝学的手法の蓄積には制約があり、近年急速に発展してきたゲノム解析注2)やトランスクリプトーム解析注3)などの大規模なデータ基盤は十分に整備されていません。
特に神経系の発生は、複数の細胞系列が精密に分化、配置される過程であり、限られた数の神経細胞やそのターゲットとなる細胞が時間とともに変化していくため、網羅的に捉えることが難しい研究対象です。実際にウニ胚や幼生においては、神経細胞は全細胞の中で相対的に少数であるため、単一細胞RNAシーケンス解析(scRNA-seq)注4)を行っても神経クラスターが小さくなり、神経分化を駆動する転写因子やシグナル経路を同定する際の感度が課題となっていました。そこで本研究では、発生段階を通したscRNA-seqアトラス(細胞分布データ集)の構築に加え、解析で見えにくい細胞集団を見えやすくするために、神経分化に強く関与するDelta–Notch経路注5)を実験的に抑制して神経細胞系列を増やし、ウニ神経発生の分子基盤をより高解像度で捉えることを目指しました。
研究内容と成果
本研究ではまず、バフンウニ(Hemicentrotus pulcherrimus)の受精後24、36、48、72、96時間という発生の主要段階から単一細胞データを取得し、発生が進むにつれて細胞集団がどのように分岐し、多様化していくのかを可視化できるscRNA-seqアトラス注6)を構築しました。これにより、ウニ胚発生における細胞状態の連続的変化を単一細胞解像度で追跡できるだけでなく、細胞種・細胞系列ごとに特徴的な遺伝子発現プロファイルを参照できる「地図」として機能する基盤が整いました。
次に、胚に対して、Delta–Notch経路(細胞間の相互作用)を阻害する薬剤処理を行い、神経分化が増強される条件を作り出しました。その結果、神経系に相当する細胞集団が相対的に増加し、通常条件では小さくなりがちな神経関連クラスターや、その中で発現する神経分化関連遺伝子がより明確に検出できるようになりました。これは、scRNA-seqの弱点である「少数細胞集団の見えにくさ」を実験操作で補い、神経発生の分子制御の理解を促す有効なアプローチであることを示しています。
このようにして得られた単一細胞データは、研究活動に幅広く活用できるよう、日本産ウニのゲノムデータベースHpBaseにて公開し、フリーソフトKana注7)を用いて解析できるプロトコルを示しました(参考図)。これにより、特定の遺伝子の発現がどの細胞集団で、どの発生段階に現れるのかを直感的に探索でき、計算解析に不慣れな研究者でも実験計画や仮説検証に利用しやすくなります。また、scRNA-seqアトラスを参照として用いることで、細胞集団全体を平均した解析(バルクRNA-seq)の結果から細胞タイプ組成の変化を推定する枠組みも提示し、従来のバルク解析とscRNA-seqを橋渡しする実用的な解析フローを確立しました。
今後の展開
本研究成果は、ウニ神経発生の理解を深めるだけでなく、非モデル生物におけるscRNA-seqの活用を促進し、発生・進化・比較生物学を横断した研究展開に資する基盤になると期待されます。
参考図
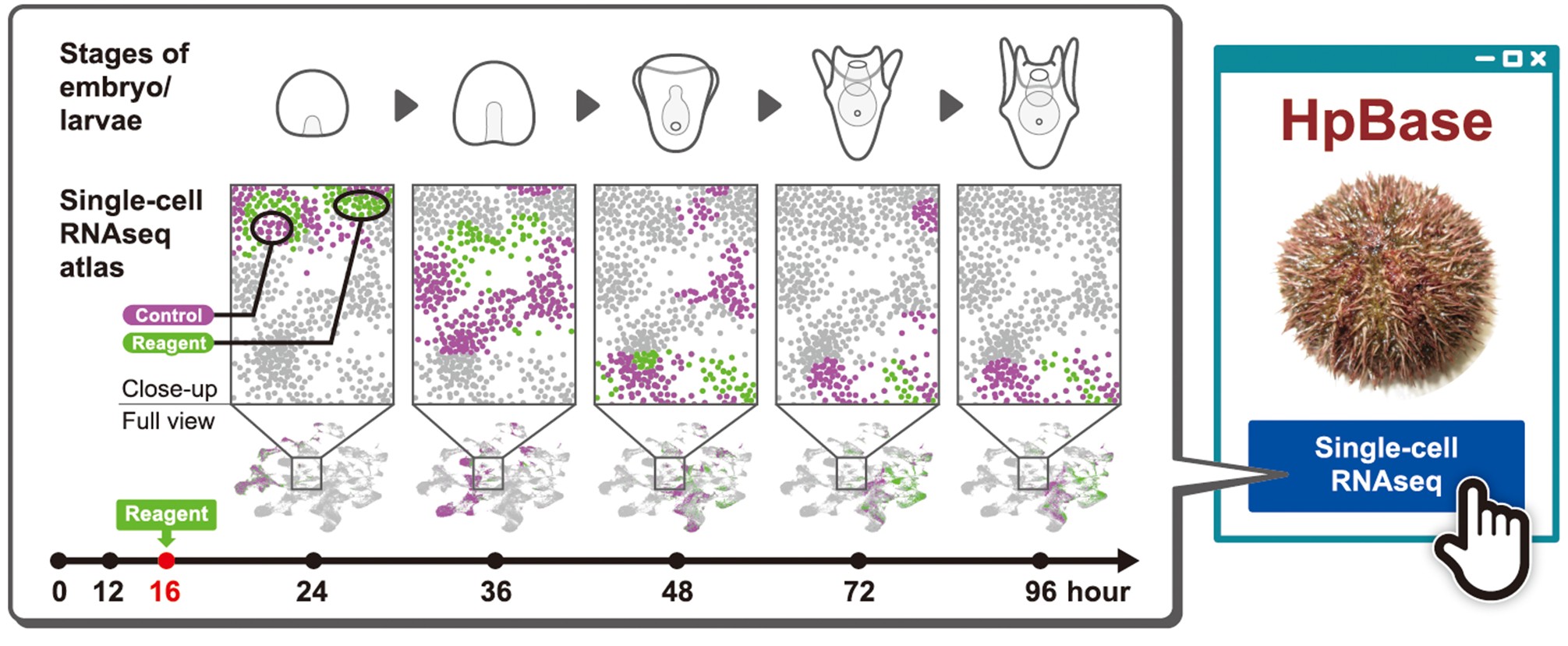
図 本研究で構築したウニ胚と幼生の単一細胞RNA-seq(scRNA-seq)アトラス
ウニ胚と幼生の発生ステージ(Stages of embryo/larvae、上段)に沿って、受精後24、36、48、72、96時間における細胞集団のscRNA-seq解析結果をアトラス(Single-cell scRNA-seq atlas)として整理した。各時点の細胞は、対照(Control、紫)と薬剤処理(Reagent、緑)で色分けして示した。薬剤は受精後16時間に添加し、その後の細胞状態の変化を単一細胞レベルで比較できる。特定領域を拡大すれば、処理条件ごとに目立つ細胞集団の変化を直感的に把握できる。得られたscRNA-seqアトラスはデータベースHpBase上で公開し、ブラウザ上で遺伝子発現の探索が可能。
用語解説
注1) 発生生物学
たった一つの細胞である受精卵から体が形作られるまでの分子メカニズムを 解明する学問。細胞内外のシグナル分子の働きと、DNAに結合して遺伝子発現を調節する転写因子の機能解析などを通じて、時間的空間的にその生物個体に何が起きているのかを明らかにする。
注2) ゲノム解析
生物がもつ全DNA配列(ゲノム)を読み取り、遺伝子の種類、配置、変異を調べる解析。これにより生物の形質や進化、疾患、適応の基盤を理解する。
注3) トランスクリプトーム解析
細胞や組織で実際に転写されている全RNA(主にmRNA)を網羅的に測定する解析。どの遺伝子がどれくらい使われているかを示し、発生段階、細胞種、条件差による発現変化を捉える。
注4) 単一細胞RNAシーケンス(scRNA-seq)
多細胞生物の体を構成する細胞に発現しているmRNAを細胞ごと網羅的に解析する手法。
注5) Delta-Notch経路
隣接する細胞が相互作用することで互いに異なる運命をもたらすメカニズムで、多くの動物の神経細胞分化の過程で見られる。DeltaとNotchはいずれも細胞膜上の膜タンパク質で、隣接する一方の細胞のDeltaがもう一方の細胞のNotchと結合することで、この細胞でのDeltaの発現を抑制し、役割の異なる細胞を分化させる。
注6) アトラス
細胞・組織・遺伝子発現などを網羅的にまとめたデータ集。単一細胞RNA-seqアトラスは、発生段階や臓器ごとに、存在する細胞タイプや遺伝子発現の分布を細胞単位で示す参照地図。
注7) Kana
scRNA-seqの結果をブラウザ上で直感的に閲覧・探索できるフリーソフト。遺伝子の発現パターン、クラスター(細胞集団)、細胞タイプの違いを可視化できる。
研究資金
本研究は、科学技術振興機構(JST) 戦略的創造研究推進事業 さきがけ「多細胞システムにおける細胞間相互作用とそのダイナミクス」研究領域(JPMJPR194C, JPMJPR1945;2019-2022年度)、科学技術振興機構(JST) 研究成果展開事業が助成するA-STEP(JPMJTR204E; 2019-2024年度)、日本学術振興会が助成する科学研究費基盤研究(B)(23K23933; 2022-2025年度)、(C)(23K11312;2023-2027年度)、(若手)(19K20406: 2019-2022 年度)による助成によって実施されました。
掲載論文
【題 名】 Single-cell transcriptomic resources for tracing neurogenesis and cell fate specification in sea urchin embryos
(ウニ胚における神経形成と細胞運命決定を解析するための単一細胞RNA-seqリソース)
【著者名】 *Koki Tsuyuzaki, Junko Yaguchi, Takashi Yamamoto, Kazuho Ikeo, *Shunsuke Yaguchi
(*責任著者)
【掲載誌】 Development
【掲載日】 2026年2月26日
【DOI】 10.1242/dev.205025
【問い合わせ先】
【研究に関すること】
谷口 俊介(やぐち しゅんすけ)
筑波大学生命環境系/下田臨海実験センター 准教授
TEL: 0558-22-1317
URL: https://sites.google.com/site/yaguchisea/home
X@urchin_lab
【取材・報道に関すること】
筑波大学 広報局
TEL: 029-853-2040
E-mail: kohositu@un.tsukuba.ac.jp
千葉大学 広報室
TEL: 043-290-2018
E-mail: koho-press@chiba-u.jp
広島大学 広報室
TEL: 082-424-4518
E-mail: koho@office.hiroshima-u.ac.jp
国立遺伝学研究所
TEL: 055-981-5873
E-mail: prkoho@nig.ac.jp

 Home
Home