<研究に関すること>
大学院統合生命科学研究科 教授 坊農 秀雅
Tel:082-424-4013
E-mail:bonohu@hiroshima-u.ac.jp
本研究成果のポイント
・真菌(病原菌やキノコ、酵母などが含まれる)で実際に発現している遺伝子の機能を解析する新しい手法を開発し、従来より多くの遺伝子の働きを明らかにできることを確認した。
・ゲノム編集(※1)標的探索など、バイオテクノロジー応用への活用が期待される。
概要
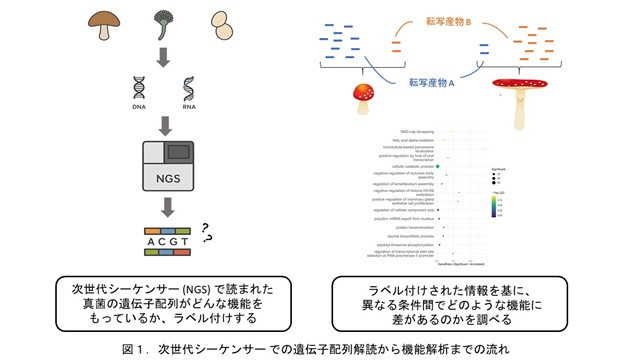
広島大学大学院統合生命科学研究科の森原なぎさ大学院生と坊農秀雅教授(広島大学大学院統合生命科学研究科・プラチナバイオ共同研究講座教授兼任)らは、真菌トランスクリプトーム(※2)のための、新たな機能注釈(※3)ワークフロー(※4)を開発した。
本研究では、シイタケおよびダイズさび病菌のトランスクリプトームデータを用いて開発したワークフローを評価し、転写産物から予測されたタンパク質コード配列(※5)の96%以上に機能注釈を付与することに成功した。これは、遺伝子がどのようなタンパク質を作り、どのような生物学的役割を持つのかを推定するものである。また、特定の条件でのみみられる転写産物や、近縁種でも発見されている転写産物など、従来手法とは異なるアプローチでの注釈も可能になっている。
本成果は、2026年2月6日に国際学術誌「Journal of Fungi」のオンライン版に掲載された。
[発表論文]
・著者:Nagisa Morihara1), Hidemasa Bono1)2)*
* Corresponding author (責任著者)
1)広島大学大学院統合生命科学研究科
2)ゲノム編集イノベーションセンター
・論文タイトル:Functional Annotation Workflow for Fungal Transcriptomes
・掲載誌: Journal of Fungi
・DOI: https://doi.org/10.3390/jof12020116
背景
真菌類は、バイオテクノロジー、農業、環境保全、ヒトの健康など、多岐にわたる分野で重要な役割を担う一方、多くの種がゲノムや遺伝子機能が解明されていない非モデル生物である。次世代シーケンサー(※6)のRNA-seq(※7)技術によってトランスクリプトームの配列決定が容易になったが、得られた配列データから遺伝子機能を推定する機能注釈は依然として課題であり、既存の生物種を限定しないツールでは、真菌特有の特徴を十分とらえきれない、注釈できず機能未知となる割合が高くなるなどの問題があった。その結果、そのあとに続く機能エンリッチメント解析(※8)、ゲノム編集などの障害となっていた。
研究成果の内容
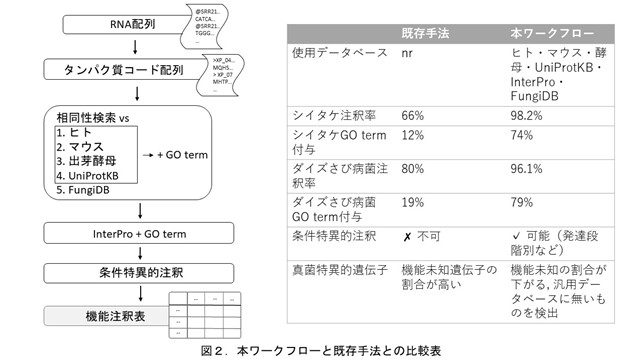
本ワークフローでは、ヒト、マウス、酵母の参照配列、タンパク質データベース(UniProtKB)、タンパク質ドメインデータベース(InterPro)、真菌に特化したデータベース(FungiDB)それぞれについて、SAQEワークフロー(※9)をベースに相同性検索を行い、転写産物から予測されたタンパク質コード配列に機能IDを付与した。さらに割り当てられたIDに対応する生物学的機能を表す共通用語であるGO termを付与し、発達段階や組織など条件特異的な注釈も実施した。
このワークフローをシイタケ57サンプルのRNA-seqデータに適用し、227,580個の転写産物から予測されたタンパク質コード配列のうち98.2%に注釈を付与(従来手法では66%)した。さらにGO termは74%に付与できた(従来手法では12%)
また菌糸体(※10)、原基(※11)、子実体(※12)のグループ間で差があった機能を解析し、菌糸体からの原基形成ではNADキャップ脱離や脂肪酸α酸化、原基からの子実体形成では有糸分裂、細胞壁リモデリング、オートファジーといった、シイタケの発達に重要な機能を同定できた。また発達段階特異的に注釈されたもののうち、胞子形成および酸化ストレス応答に関与する、酵母SWS2遺伝子のホモログ(※13)が原基でのみ発現していることがわかった。これらの結果は、これまでの手法では機能注釈できず見逃されていた転写産物を発見できる能力を本ワークフローが有していることを示している。
続いてダイズさび病菌のIso-Seq(※14)データへも適用し、9,680個のタンパク質コード転写産物のうち96.1%に注釈を付与できた(従来手法では80%)。さらにGO termは79%に付与できた(従来手法では19%)。感染後に発現が下がる転写産物の機能を調べたところ、K48結合型ユビキチン化の負の制御、細胞接着分子生産、ヒストン脱アセチル化など、病原性に関わる制御機構を同定した。またFungiDBでのみ注釈されたさび病菌やその他病原菌由来の機能未解明遺伝子は、さび病菌における新規機能の存在を示唆するとともに、将来的なゲノム編集標的候補となる可能性を示している。
今後の展開
公共データベースに蓄積されたRNA-seqデータを本ワークフローで再解析することにより、未探索の転写産物の発見が期待される。
また本手法により優先順位付けされた候補遺伝子は、ゲノム編集技術などに適用されることで基礎研究から応用研究への橋渡しを促進する。例えば、食用きのこの品種改良、植物病原菌の制御、有用代謝産物の生産など、バイオテクノロジー分野への応用が期待される。
参考資料
用語解説
(※1)ゲノム編集:ゲノムを構成するDNAを切断し、遺伝子を書き換える技術。
(※2)トランスクリプトーム:DNAから転写された全てのRNA。全転写産物。
(※3)機能注釈:DNAまたはRNA配列がどのような働きを持つかをラベル付けするプロセス。
(※4)ワークフロー:データ解析において、複数のプログラムを順序だてて組み合わせたもの。
(※5)タンパク質コード配列:DNAまたはRNA配列のうち、タンパク質を構成するアミノ酸の順序情報を持つ部分。
(※6)次世代シーケンサー:DNAやRNA配列を一度に大量に解読する装置。
(※7)RNA-seq:次世代シーケンサーを用いて、DNAから転写されたRNAの配列や量を解析する技術
(※8)機能エンリッチメント解析:発現変動遺伝子リストにおいて、どんな機能に有意に偏っているかを明らかにする。
(※9)SAQEワークフロー:https://github.com/bonohu/SAQE
(※10)菌糸体:キノコやカビなどの菌類における、細い糸状の菌糸の集合体。
(※11)原基:菌糸体が凝集して形成される、きのこの基のこと。
(※12)子実体:いわゆるきのこの実の部分のこと。
(※13)ホモログ:進化の過程で比較的保存された、似た配列の遺伝子。
(※14)Iso-Seq:全長転写産物配列を読む手法。
- 【プレスリリース】真菌の遺伝子機能注釈を向上させる新手法を開発 ―シイタケおよびダイズさび病菌を例に―.pdf(429.86 KB)
- 掲載誌:Journal of Fungi
- 研究者ガイドブック(坊農 秀雅 教授)

 Home
Home